NCBI BLAST 搜索结果页面详解:从入门到精通
来源:武汉市灰藻生物科技有限公司 浏览量:57 发布时间:2026-04-27 10:56:16
引言
BLAST(基本局部比对搜索工具)是目前最常用的序列相似性搜索工具之一,几乎所有从事分子生物学、基因组学或生物信息学研究的科研人员都曾使用过它。然而,当搜索任务提交完成后,面对返回的结果页面——那些密密麻麻的表格、选项卡、筛选条件和比对图形——许多初学者甚至经验丰富的用户都难免感到困惑:哪些信息是最关键的?不同选项卡之间有什么区别?为了帮助大家真正读懂BLAST结果,本文基于NCBI官方发布的《BLAST结果页面注解》文档,对结果页面的各个区块和元素进行了系统梳理和详细解读。本文旨在结合学术术语的中英文对照,为国内科研人员提供一份清晰、实用、可随时查阅的BLAST结果解读指南。无论您是初次接触BLAST,还是希望进一步掌握高级筛选和比对查看技巧,相信本文都能为您提供有益的帮助。
摘要区块(Summary Section)
页眉(Header)
页眉包含三级导航链接:顶部蓝色条带为NCBI全局导航,中间灰色条带为BLAST全局导航,底部白色条带为当前BLAST结果专属导航。
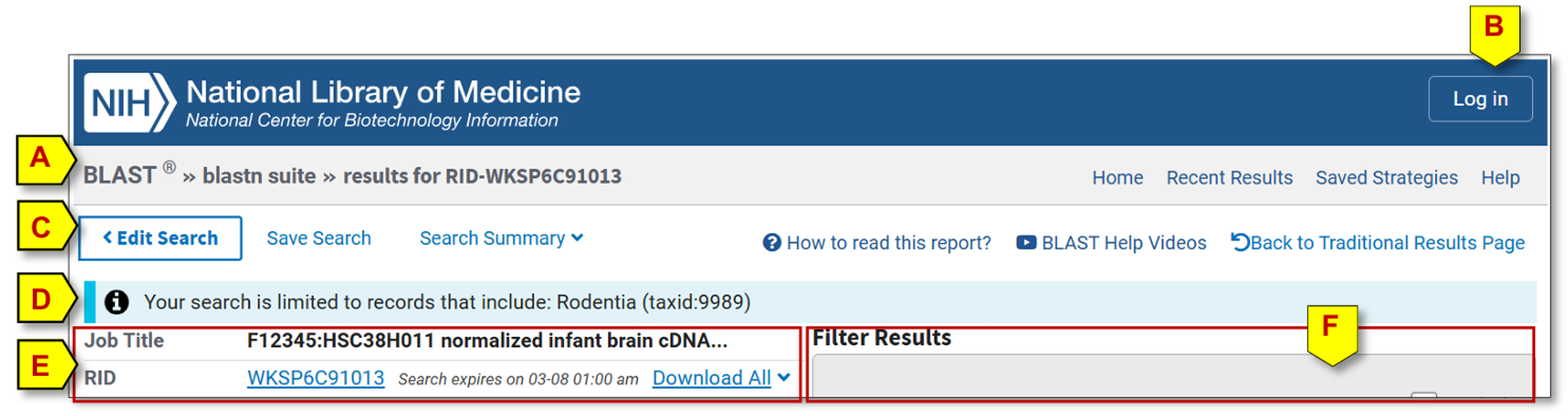
A. 顶部导航链接
• 面包屑导航(Breadcrumbs):展示当前结果页面的层级路径。
• 关键BLAST页面链接:
o “Home”:返回BLAST首页。
o “Recent Results”:以表格形式列出近期提交的BLAST搜索记录,包含关键属性及过期时间。
o “Saved Strategies”:用于保存搜索策略,配合MyNCBI账户登录使用效果最佳。
o “Help”:提供指向各类BLAST相关文档的链接集合。
B. 登录MyNCBI账户
可永久保存搜索设置,并查看登录期间执行的所有未过期的搜索结果。
该区域顶部有一组链接(C),其下方(如有)会显示高亮提示或错误信息(D)。再往下,左侧为关键搜索属性(E),右侧为结果筛选器(F)。无论下方选择哪个结果选项卡,本区域始终显示。
C. 摘要区域顶部链接
• Edit Search:打开搜索页面并保留之前设置,便于调整参数后重新运行。
• Save Search:将当前搜索设置保存到“已保存搜索策略”页面;配合MyNCBI登录可永久保存。
• Search Summary:展开/收起一个表格,汇总搜索设置和统计信息。
• How to read this report:链接到本文档。
• BLAST Help Videos:打开NLM(美国国家医学图书馆)频道中BLAST相关视频的YouTube播放列表。
• Back to Traditional Result Page:以传统单页面格式呈现结果。
D. 重要提示或错误信息
若存在重要的搜索修改(如限定物种、针对短序列的调整),将在此处显示。如果搜索失败,也会在此处以粉红色背景显示错误信息(1)。

链接和消息下方是关键属性搜索摘要(A)和结果筛选器(B)。无论下方选择哪个结果选项卡(C),本区域始终显示。
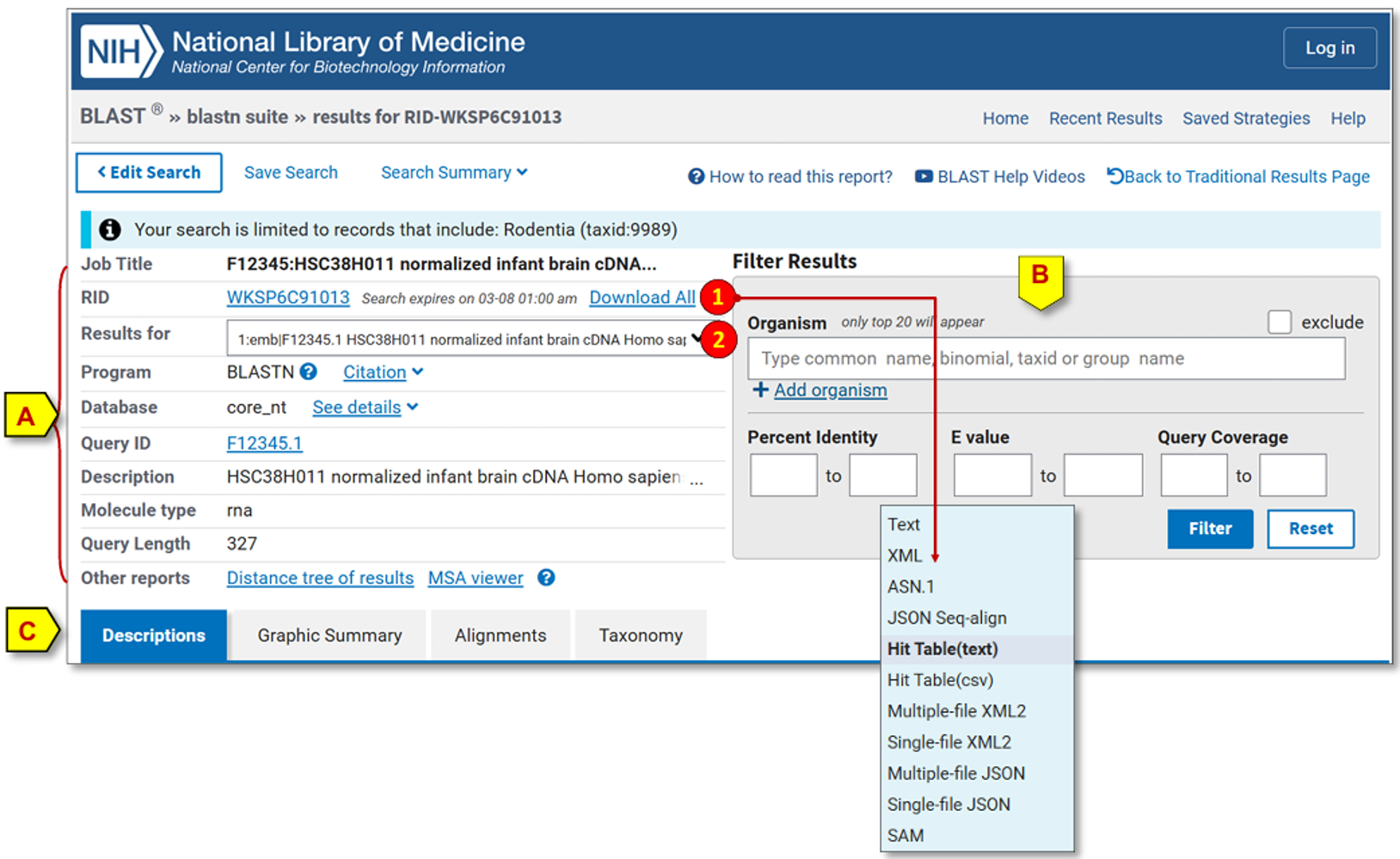
A. 摘要——提供搜索的不同方面信息
• Job Title(任务标题):默认显示第一条查询序列的ID;为便于识别,可在提交前自定义。
• RID(请求标识符):本次搜索分配的唯一标识符,用于共享和问题报告;Download All(下载全部)(1)提供将完整搜索结果保存为多种格式的选项,如新版XML(XML2)、JSON、CSV。
• Results for(结果对应查询)(2):仅当提交多条查询序列时显示,允许选择展示哪一条查询序列的搜索结果。
• Program(程序):列出所执行的搜索程序,此处示例为BLASTN;Citation(引用):提供发表时需引用的参考文献。
• Database(数据库):所搜索的目标数据库名称;See details(查看详情):提供数据库内容的文本描述。
• Query ID(查询ID):当前显示结果所对应的查询序列ID。若查询为accession号格式,则会链接到NCBI数据库中的该记录。
• Description(描述):查询序列FASTA标题行中的描述信息。
• Molecule type(分子类型):显示查询序列的类型(DNA或蛋白质)。
• Query length(查询长度):当前查询序列的长度。
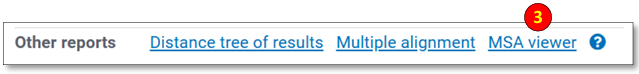
• Other reports(其他报告):列出未集成到新版选项卡显示中的其他报告格式链接。蛋白质BLAST结果会额外提供“Multiple alignment(多重比对)”链接(3),可将查询序列与匹配序列提交至NCBI的多重比对工具COBALT进行多重比对。
B. 筛选结果(Filter Results)
• Organism(物种):允许输入物种名称(从自动提示列表中选择),用于筛选返回的匹配序列。勾选exclude(排除) 复选框可排除所选物种。点击Add organism(添加物种) 可增加输入框。
• Percent Identity(一致性百分比):按一致性程度筛选匹配序列,例如筛选一致性在94.74%到94.76%之间的结果。
• E Value(期望值):按期望值(E值)显著性筛选结果,例如筛选期望值在0.0001到5e-120(即5×10⁻¹²⁰的科学记数法)之间的结果。
输入期望的数值后,点击Filter(筛选) 即可更新结果展示。筛选基于后处理,不会改变由RID标识的原始搜索结果。点击Reset(重置) 可恢复初始结果集。
描述表格(Descriptions Table)
这是默认打开的选项卡,包含BLAST所发现匹配序列的摘要表格。表格上方是三组下拉菜单(A)和一组用于在新浏览器标签页中展示匹配序列的功能性链接(B)。表格表头(C) 描述各列内容,并支持按选定列排序。
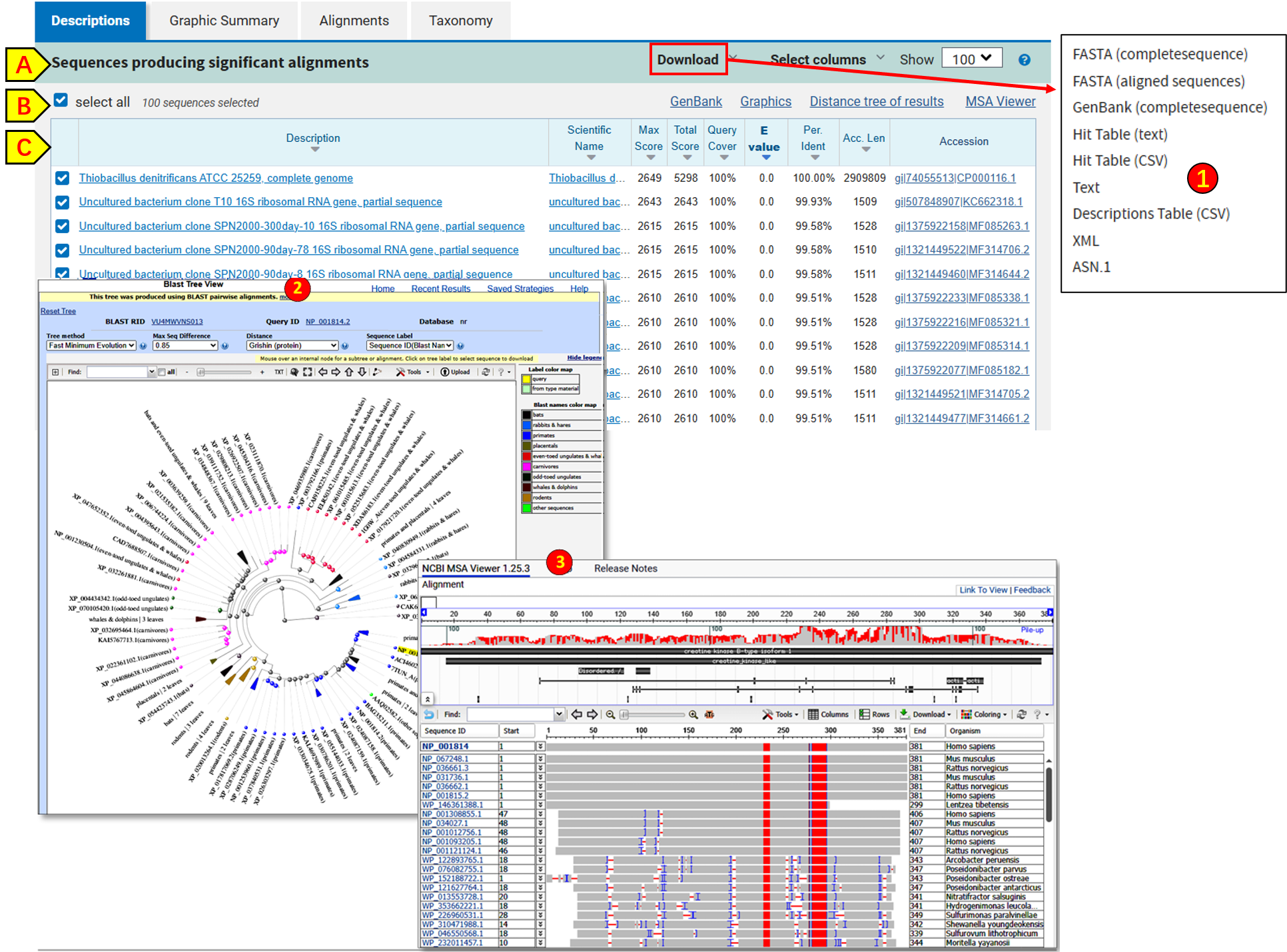
A. 顶部下拉菜单
• Download(下载):提供以多种格式下载复选框选中的匹配序列的选项,也包括下载当前表格本身(1)。此选项与 “Download All”中的选项不同。
• Manage Columns(管理列):列出表格所有可用列,便于自定义显示的列。
• Show(显示):允许选择表格中显示多少条匹配序列。
B. 针对本次搜索的功能性链接
• Select All(全选):切换所有匹配序列复选框的选中状态。点击单个复选框可单独选中或取消选中某条记录。
• GenPept(GenBank蛋白质)(对于核苷酸搜索则为GenBank):从蛋白质数据库中检索所选匹配序列的完整记录。
• Graphics(图形):打开基于序列可视化工具的图形化视图,以查询序列为锚点展示匹配情况。
• Distance tree of results(结果距离树):以距离树格式展示匹配序列(2)。
• Multiple alignment(多重比对):将查询序列与匹配序列提交至COBALT进行多重比对。
• MSA Viewer(多重序列比对查看器):打开多重序列比对查看器(3),允许对比对结果进行详细的交互式检视。
C. 表格表头与行
• 描述(Description) 列中的标题链接到比对(Alignments) 选项卡中相应的比对记录。点击标题即可跳转至该比对,查看详细比对信息。
• 第二列中的物种学名(Scientific Name) 链接到NCBI分类数据库中的对应记录。
• 默认按E值(E value) 排序(该列以粗体显示)。点击其他列表头可按该列排序(不支持多列组合排序)。
• Accession(登录号) 列中的条目链接到蛋白质数据库(对于blastn或tblastn搜索则为核苷酸数据库)中的序列记录。
比对选项卡(Alignments Tab)
比对(Alignments) 区块包含查询序列与其匹配序列之间的详细两两比对。
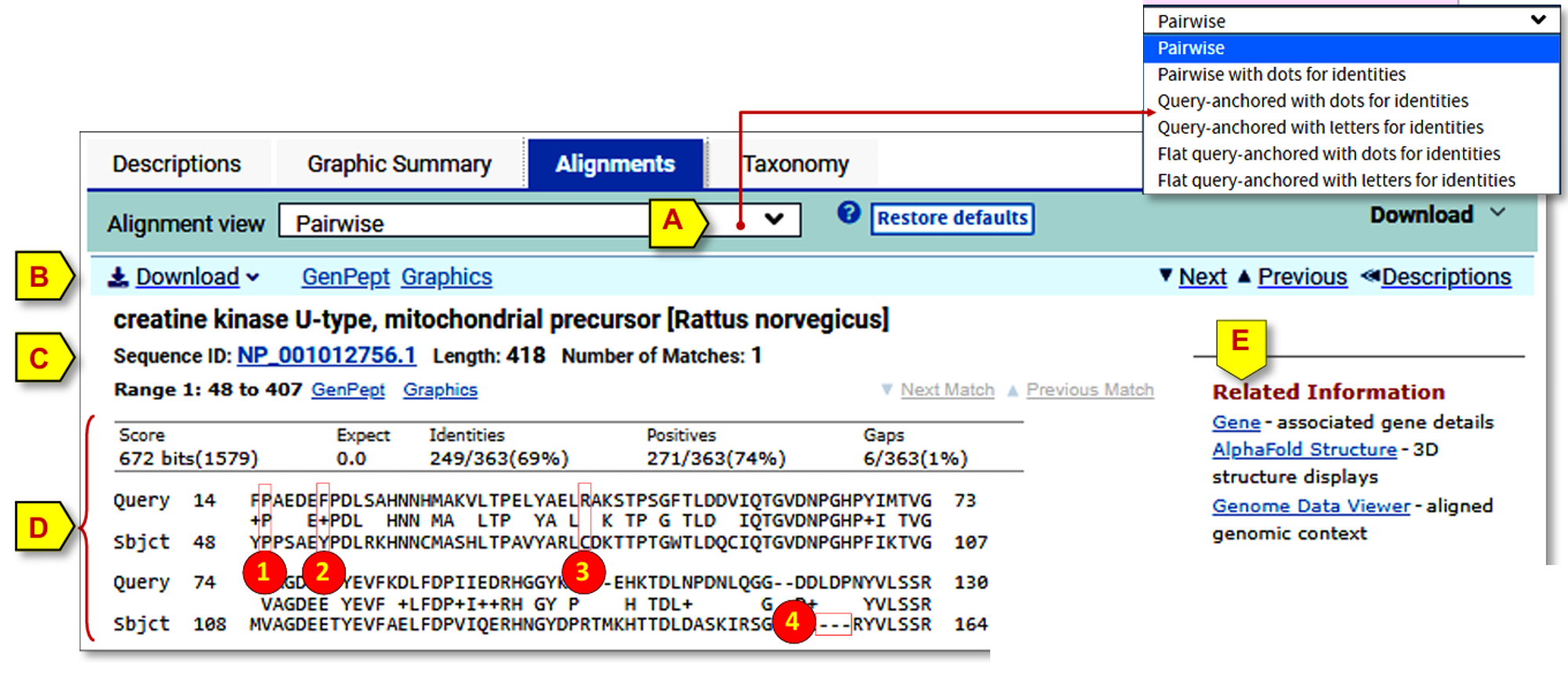
A. 比对视图(Alignment view)
通过一个简单的下拉菜单,可方便地切换比对结果的不同展示形式。
B. 匹配的数据库序列分隔条
• Download(下载):列出可用于获取该匹配数据库序列的格式选项。
• GenePept(GenBank蛋白质)(对于核苷酸搜索则为GenBank):从NCBI蛋白质数据库中检索该序列记录。
• Graphics(图形):打开基于序列可视化工具的图形化视图,以该数据库序列为锚点展示比对。
• 右侧的导航链接可在不同比对记录之间跳转,也可在比对(Alignments) 和描述(Descriptions) 区块之间切换。
C. 匹配的数据库序列(Matched database sequence) D. 比对展示(Alignment display)
• 迷你选项卡(Mini-tab):包含比对的统计信息。
• 中间行报告匹配质量:
o 字母表示完全一致(1,即相同碱基/氨基酸)
o + 号表示正向匹配(2,相当于保守替换)
o 空格表示得分为零或负分的匹配(3)
o 序列中的短横线(-) 表示空位(4)
E. 相关信息(Related Information)
包含指向其他资源的链接,这些资源基于匹配的数据库序列衍生出更多信息。
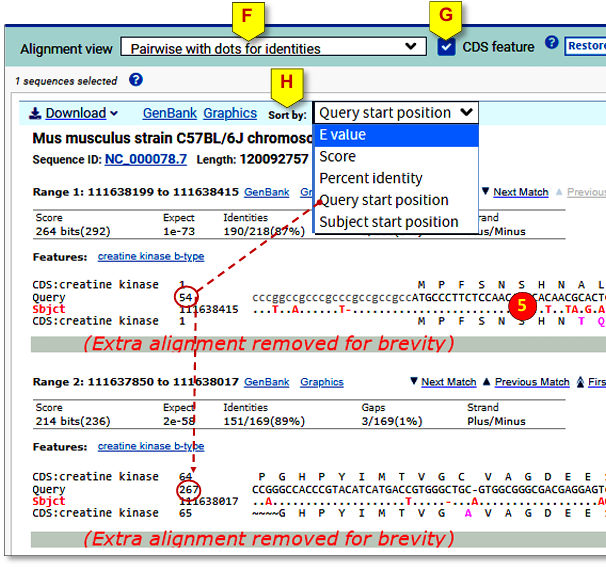
F. 比对视图(Alignment view)
改变比对的呈现方式。“Pairwise with dots for identities”(用点表示一致的两两比对) 模式以彩色字母高亮差异(5),便于识别。
G. “CDS feature”(CDS特征)复选框(仅适用于核苷酸BLAST)
若存在注释信息,可将已注释的编码序列翻译结果投射到比对中。
H. “Sort by”(排序方式)
允许按其他数值对HSP(高分段对,High Scoring Pair)进行排序,而非默认的E值。一条查询序列可能与同一条数据库序列存在多个HSP。例如,一条mRNA与其基因组序列比对时,由于内含子的存在,比对会被分割成多个HSP。按“Query start position”(查询起始位置) 重新排序,有助于按照mRNA的自然/生物学顺序来检视这些比对。
结语
BLAST结果页面虽然信息密集,但只要理解了其固定的结构逻辑——顶部的摘要与筛选、默认的“描述”表格、以及详细的“比对”视图——就能快速从中提取出对自己研究最有价值的信息。希望本文能成为您科研路上的一本顺手工具书,让BAST结果不再“高深莫测”。祝您比对顺利,发现精彩!
参考文献
https://ftp.ncbi.nlm.nih.gov/pub/factsheets/HowTo_BLAST_NewResultPage.pdf
相关阅读
如何进行微生物序列分析?FASTA和BLAST理论介绍,及公共数据库16S序列分析操作教程
细菌16S rRNA测序能否鉴定到属种(species),为什么保藏中心将16S测序作为鉴定依据?
敬请关注灰藻生物,共筑健康未来!
— 武汉市灰藻生物科技有限公司团队敬上
灰藻生物:我们期待着与客户共同成长,共创生命科学的美好未来!
更新日期:2026-04-25
编制人:小灰
审稿人:小藻
