分子实验笔记13:Gibson Assembly 克隆(Gibson Assembly Cloning)
来源:武汉市灰藻生物科技有限公司 浏览量:186 发布时间:2026-03-25 21:17:06
引言(Introduction)
2009年,J. Craig Venter研究所的Daniel Gibson博士及其同事开发了一种新颖的方法,用于高效组装多个线性DNA片段(Gibson et al., 2009)。
无论片段长度或末端兼容性如何,多个具有重叠序列的DNA片段均可在**单管、等温反应**(single isothermal reaction)中一步拼接。
该方法利用三种不同酶的协同作用,最终产物为**完全连接的双链DNA分子**。这一技术已被证明是构建质粒的高效手段,现已被分子生物学家广泛采用。
为何选择Gibson克隆?(Why Gibson Cloning?)
- 无需特定限制性酶切位点(restriction sites):可连接几乎任意两个DNA片段,不受序列限制;
- 无缝连接(No scar):拼接处无额外碱基残留;
- 步骤简便:单管反应,操作流程短;
- 多片段同步组装:可一次性连接多个DNA片段。
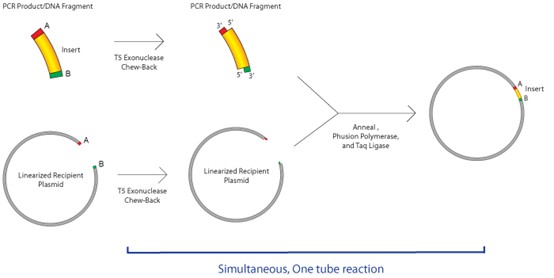
Gibson 克隆
操作流程(Procedure)
- 设计质粒并订购引物(参见下方示意图)
设计时需明确最终质粒由哪些DNA片段拼接而成。相邻片段末端应包含**相同的重叠序列**(如图中序列A和B)。这些重叠区可通过PCR引入:引物5'端包含与相邻片段匹配的序列,3'端则与目标模板退火。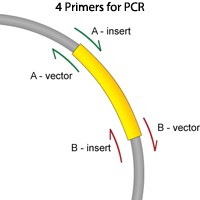
- 通过PCR扩增各DNA片段。
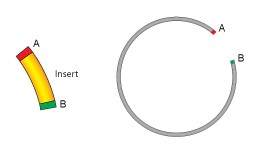
图3:通过PCR扩增各DNA片段
- 琼脂糖凝胶电泳检测PCR产物,确认大小与产量。若存在明显非特异条带,需进行凝胶纯化;若产物单一,可直接使用PCR纯化产物,甚至未经纯化的PCR反应液(raw PCR mix)也可用于组装以节省时间。
- 在冰上配制Gibson Assembly反应体系,加入各DNA片段。
- 将反应产物转化至感受态细菌,并通过限制性酶切筛选正确重组质粒。
- 对最终质粒的关键区域进行测序验证,尤其是各组装片段的连接处(seams)。
小技巧(Tips and Troubleshooting)
- 使用寡核苷酸“缝合”片段(“Stitching” fragments together using oligos)
- 单次反应可组装的片段数量
参考文献
- New England Biolabs (NEB) 提供多种DNA组装试剂盒及预混液,包括 NEBuilder HiFi 和 Gibson Assembly,同时也提供 ET SSB。NEB还提供引物设计工具等资源。Gibson Assembly® 技术由 TelesisBio 授权 NEB 销售。
- Gibson DG, Young L, Chuang RY, Venter JC, Hutchison CA, Smith HO. (2009). Enzymatic assembly of DNA molecules up to several hundred kilobases. Nature Methods, 6(5), 343–345. https://doi.org/10.1038/nmeth.1318
- Gibson DG, Smith HO, Hutchison CA, Venter JC, Merryman C. (2010). Chemical synthesis of the mouse mitochondrial genome. Nature Methods, 7(11), 901–903. https://doi.org/10.1038/nmeth.1515
- Rabe BA, Cepko C. (2020). A Simple Enhancement for Gibson Isothermal Assembly. bioRxiv. https://doi.org/10.1101/2020.06.14.150979
敬请关注灰藻生物,共筑健康未来!
— 武汉市灰藻生物科技有限公司团队敬上
灰藻生物:我们期待着与客户共同成长,共创生命科学的美好未来!
更新日期:2026-02-27
编制人:磊子
审稿人:小藻
